ChIP Sequencing
特長
・転写調節因子やヒストン修飾の研究で利用される網羅的なクロマチン免疫沈降サンプルのシーケンス解析。
・転写調節因子やクロマチン結合タンパク質がDNAと相互作用し、遺伝子発現を制御する機構の解明に有用。
・発現解析と組み合わせた解析もご提案可能。
解析概要
次世代シーケンサー(NGS)を用いて、クロマチン免疫沈降(ChIP)により回収されたDNAの塩基配列を決定します。得られたリード配列を参照配列にマッピングし、タンパク質の結合部位を予測します。その後、アノテーションの付与およびGO解析、モチーフの検出を行います。
解析結果
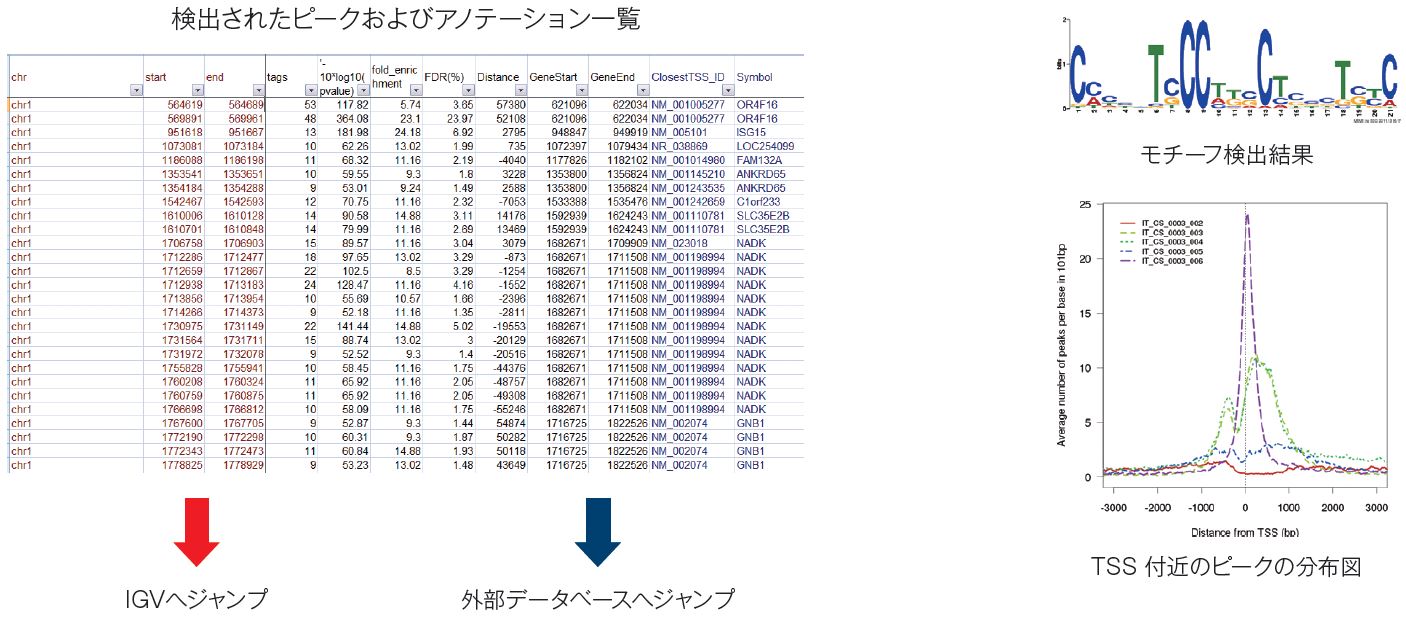
納品物
・解析報告書
・データHDD:リード情報(FASTQ)、マッピングデータ(BAM)、ピーク検出データ(BED)
ピークのアノテーションデータ(エクセル・マクロファイルとテキストファイル)、モチーフデータ
サンプル条件
| サンプルの種類 | ChIPed DNA /コントロールDNA※1 |
|---|---|
| DNA量 | 40 ng |
| 濃度※2 | 1 ng/µL以上 |
| フラグメントサイズのピーク | 700bp以下(推奨200~300bp)※3 |
| 溶媒 | 1x TE |
| 解析対象の生物種 | ヒト、マウス |
※2 サンプルの定量はQubitまたはPicoGreenを用いた方法を推奨しております。
※3 免疫沈降前の電気泳動写真がお手元にある場合にはご提出をお願いします。
解析例
| 機種 | NovaSeq 6000 |
|---|---|
| ペアリード数/サンプル | 約20M ペアリード※1 |
| リード長 | 100 bp※2 |
| シーケンス方法 | Paired End/Multiplex |
| バイオインフォマティクス解析 | コールされたピーク領域のリスト、ピークに近接する遺伝子のリスト ピーク領域に見られるモチーフ配列、GO解析データ |
| 納期 | 品質評価通過後、約3.0ヵ月※3 |
※2 バイオインフォマティクス解析時にリード長を50 bpのシングルエンドにトリミングします。
※3 同時に解析を行うサンプル数が多い場合には、別途お打ち合わせの上、決定いたします。




