がんエクソーム解析
特長
- 腫瘍検体を用いた体細胞変異解析サービスをご提供。
- 腫瘍と正常検体を解析することで、体細胞変異を特異的に検出(マッチドペア解析)。
- 腫瘍特異的な体細胞変異データを用いて、mutational signature 解析、driver 変異探索、neoantigen 探索、Tumor Mutation Burden (TMB) 算出などもオプション解析としてご提供可能。
- ヒト腫瘍細胞をマウスに移植したXenograftサンプルの変異解析も実施可能。
解析概要
体細胞変異検出を目的としたマッチドペア解析やヒト腫瘍細胞をマウスに移植したXenograftサンプルの変異解析も実施可能です。

エクソン領域濃縮キット
SureSelect All Exon
実績のあるAgilent technologies社のSureSelect All Exonを使用したサービスです。| パネル名 | 対応生物種 | 対象領域 | デザイン サイズ |
|---|---|---|---|
| SureSelect Human All Exon V6 | ヒト | コーディング領域、miRNA、snoRNA、tRNA | 60 Mb |
| SureSelect Human All Exon V6 + UTR | ヒト | V6の全対象領域、体質性疾患研究向けUTR領域 | 91 Mb |
| SureSelect Human All Exon V7 | ヒト | コーディング領域 | 48.2 Mb |
| SureSelect Human All Exon V8 | ヒト | コーディング領域、TERTプロモーター | 41.6 Mb |
| SureSelect Mouse All Exon | マウス | コーディング領域 | 49.6 Mb |
オプションバイオインフォマティクス解析(ヒトのみ対応可能)
mutational signature解析
がん細胞の変異リストから、変異およびその前後の塩基配列も加えた変異パターン(mutational signature)の抽出を行います。【主な解析結果】
最適なsignature数の判定結果、各signatureのプロファイル、各 signatureをCOSMICのreference signaturesに分解した結果、各症例におけるCOSMICのreference signaturesの寄与など
driver変異探索
ゲノム上の特定の領域に特定の変異が集積する有意性を判定することにより、driver変異の探索を行います。【主な解析結果】
各領域への変異集積の有意性を判定するための結果、遺伝子領域ごとの変異の集積結果など
neoantigen探索
腫瘍特異的な体細胞変異のデータを用いて、がん細胞に特徴的な変異ペプチドのパターン(neoantigen signature)を同定します。【主な解析結果】
MHCクラスI分子との親和性予測、既知エピトープとのホモロジー探索、T細胞受容体との結合・相互作用予測、neoantigen signatureの抽出など
TMBの算出
体細胞変異検出データから、TMB(Tumor Mutation Burden)を算出します。詳細はこちらをご参照ください。
MSI(Microsatellite Instability)解析
マイクロサテライト領域を網羅的に解析し、MSIを評価します。詳細はこちらをご参照ください。
HRD(Homologous Recombination Deficiency)解析
腫瘍特異的な体細胞変異のデータからHRD scoreを算出します。詳細はこちらをご参照ください。
PDXサンプルの変異解析
患者由来の腫瘍をマウスに移植したXenograft(Patient-derived xenograft: PDX)サンプルのシーケンスデータを用いて、変異解析を実施します。【主な解析結果】
SNVおよび一部のShort InDelの同定、各種アノテーション付与(通常の解析結果と同じ)
HLAタイピング
シーケンスデータからHLAクラスI (HLA-A, B, C)遺伝子のHLAタイピングを実施します。詳細はこちらをご参照ください。
解析結果
検出されたSNVは、各種アノテーション※2をつけてエクセル・マクロファイル※3 とテキストファイルでご提出します。
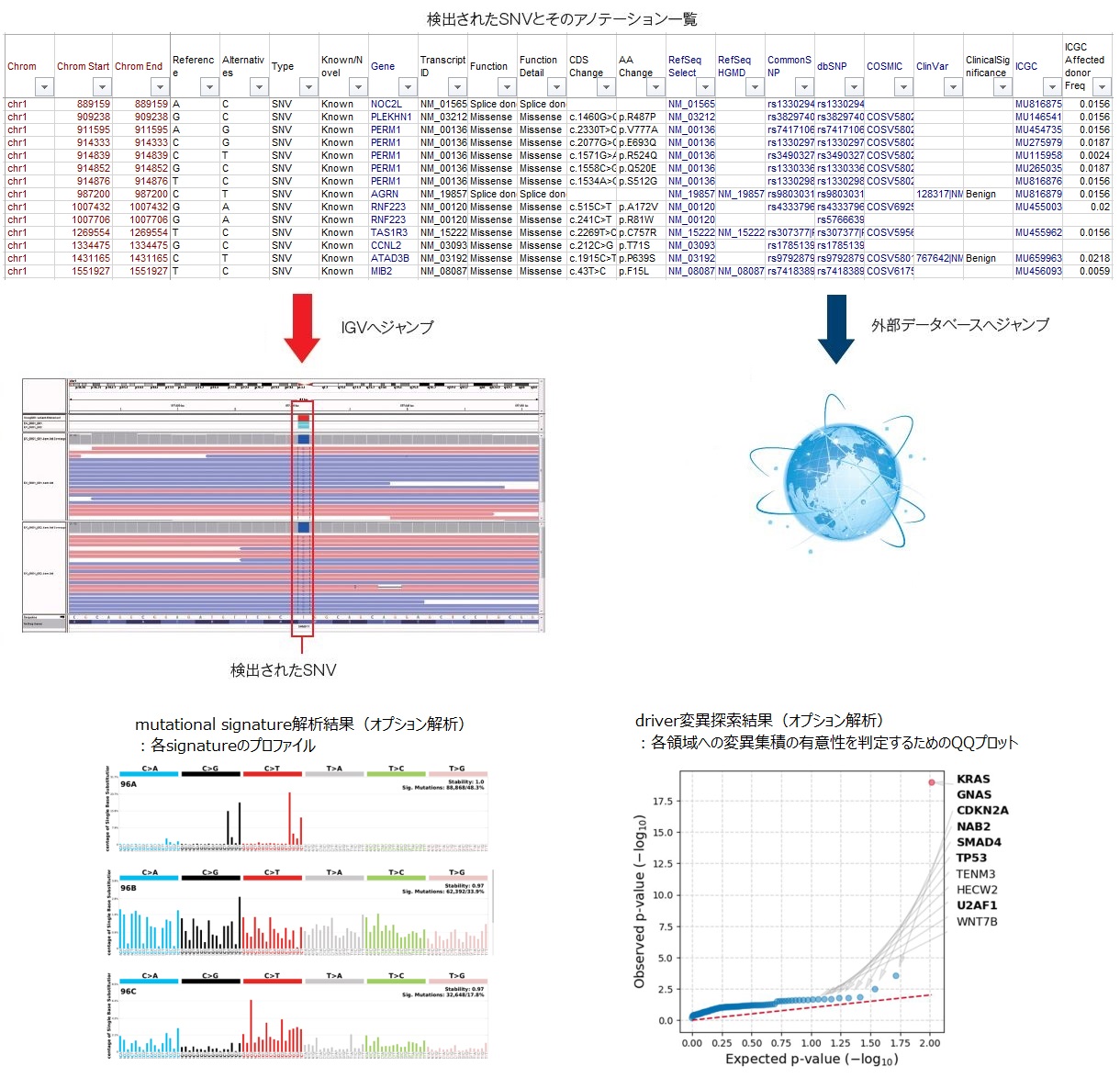
- ※1 マッピング結果、SNV、DepthはIntegrative Genomics Viewer(IGV)で閲覧することが可能です。
- ※2 検出されたSNVには次のようなアノテーションがつきます(Humanの場合)。
変異箇所、塩基、新規/既知、影響を与える遺伝子、遺伝子への影響、dbSNP ID、RefSeq ID、CCDS ID、アレル頻度(gnomAD、1000 Genomes、HGVD、GEM-J WGA)、Conserved Elements、アミノ酸置換影響予測(SIFTなど)、Splice Site変異影響予測、Depth、クオリティ値、サンプルごとのジェノタイプデータなど。 - ※3 アノテーションは弊社オリジナルのエクセル・マクロ(AnnotationViewer)で観覧でき、IGVおよび外部データベースと連携するようになっています。
納品物
- 解析報告書
- データHDD:リード情報(FASTQ)、マッピングデータ(BAM)、SNV/InDel検出データ(VCF)、SNV/InDelのアノテーションデータ(エクセル・マクロファイルとテキストファイル)
サンプル条件
| サンプルの種類 | 精製ゲノムDNA | FFPEゲノムDNA |
|---|---|---|
| DNA量 | 3 µg | 1 µg |
| 濃度 | 50 ng/µL以上 | 50 ng/µL以上 |
| OD260/280 | 1.8以上 | 1.8以上 |
| DIN値 | - | 3以上 |
- サンプルの定量はQubitまたはPicoGreenを用いた方法を推奨しております。
- サンプルの電気泳動写真がお手元にある場合にはご提供をお願いします。
- Xenograftに由来するサンプルの場合は、その旨ご連絡下さい。
解析例
| 検体数 | 2(腫瘍および正常検体) |
|---|---|
| 機種 | NovaSeq 6000 |
| Exon Capture方法 | SureSelect Human All Exon V8 |
| 平均データ量/サンプル | 約20 Gb |
| リード長 | 150 bp |
| シーケンス方法 | Paired End/Multiplex |
| バイオインフォマティクス解析 | SNV、および一部のShort InDelの同定、 各種アノテーション付与 |
| 納期 | 品質評価通過後、約2.5ヵ月※ |
- ※ 同時に解析を行うサンプル数が多い場合には、別途お打ち合わせの上決定いたします。
